Particionando a diversidade beta
Há muito tempo naturalistas e ecólogos entendem que a diversidade biológica não está homogeneamente distribuída na superfície da Terra. Dessa forma, a diversidade beta tenta entender o quão diferente (ou quão similar) é a comunidade de dois ou mais locais (ou tempos) distintos. Geralmente as métricas de diversidade beta são baseadas em similaridade, variando de zero (comunidades totalmente distintas) até um (comunidades totalmente similares).
O que torna duas comunidades distintas
Potencialmente dois processos distintos e complementares podem resultar na diferença das comunidades (Baselga and Orme 2012).
Reposição de espécies (turnover): Consiste na substituição de espécies de um local por espécies diferentes em outro local.
Perda (ou ganho) de espécies: Consiste no desaparecimento (ou aparecimento) de uma espécie em um único local, tornando assim a comunidade de menor número de espécies (menor riqueza) um subconjunto da comunidade com maior número de espécies. Esse padrão pode ser chamado de aninhamento (nestedness).
Funções do pacote betapart() (Baselga and Orme 2012)
A função desse pacote é disponibilizar um conjunto de ferramentas para calcular e particionar a diversidade beta em seus dois componentes descritos (turnover e nestedness)
Calculando os componentes e database utilizado.
Para calcular os componentes da diversidade beta iremos utilizar a Database embutida no pacote betapart() que consiste na diversidade de aves dos Estados Unidos da América nos anos de 1980 e 2000.
require(betapart) #carregar pacote
data(bbsData) #Carregar databaseObjetos utilizados
Primeiramente é necessário criar uma matriz de dissimilaridade (betapart object) baseado numa matriz de presença/ausência, necessário para outras análises utilizando a função betapart.core(). O conjunto de dados aceito para todas as funções do betapart() consiste em uma matrix (m) de presença (1) e ausência (0) de m espécies (colunas) em n locais (linhas).
#Criar objeto betapart
beta1980<- betapart.core(bbs1980) #Criando objeto da comunidade de Aves de 1980
beta2000<- betapart.core(bbs2000) #Criando objeto da comunidade de Aves de 2000Agora com os objetos criados é possível calcular a diversidade beta total e seus 2 componentes (turnover e nestedness).
bm1980<-beta.multi(beta1980, "sorensen")
bm2000<-beta.multi(beta2000,"sorensen")Função beta.pair()
Para calcular a diversidade beta total e seus componentes entre cada par de local amostrado utiliza-se a função beta.pair().
bp1980<-beta.pair(beta1980, "sorensen")
bp2000<-beta.pair(beta2000,"sorensen")Para representar graficamente a diversidade beta pode ser feito uma análise de agrupamento (clusters) com os dados já calculados.
plot(hclust(bp1980$beta.sor, method="average"), hang=-1, main='', sub='', xlab='')
title(xlab=expression(beta[sor]), line=0.3)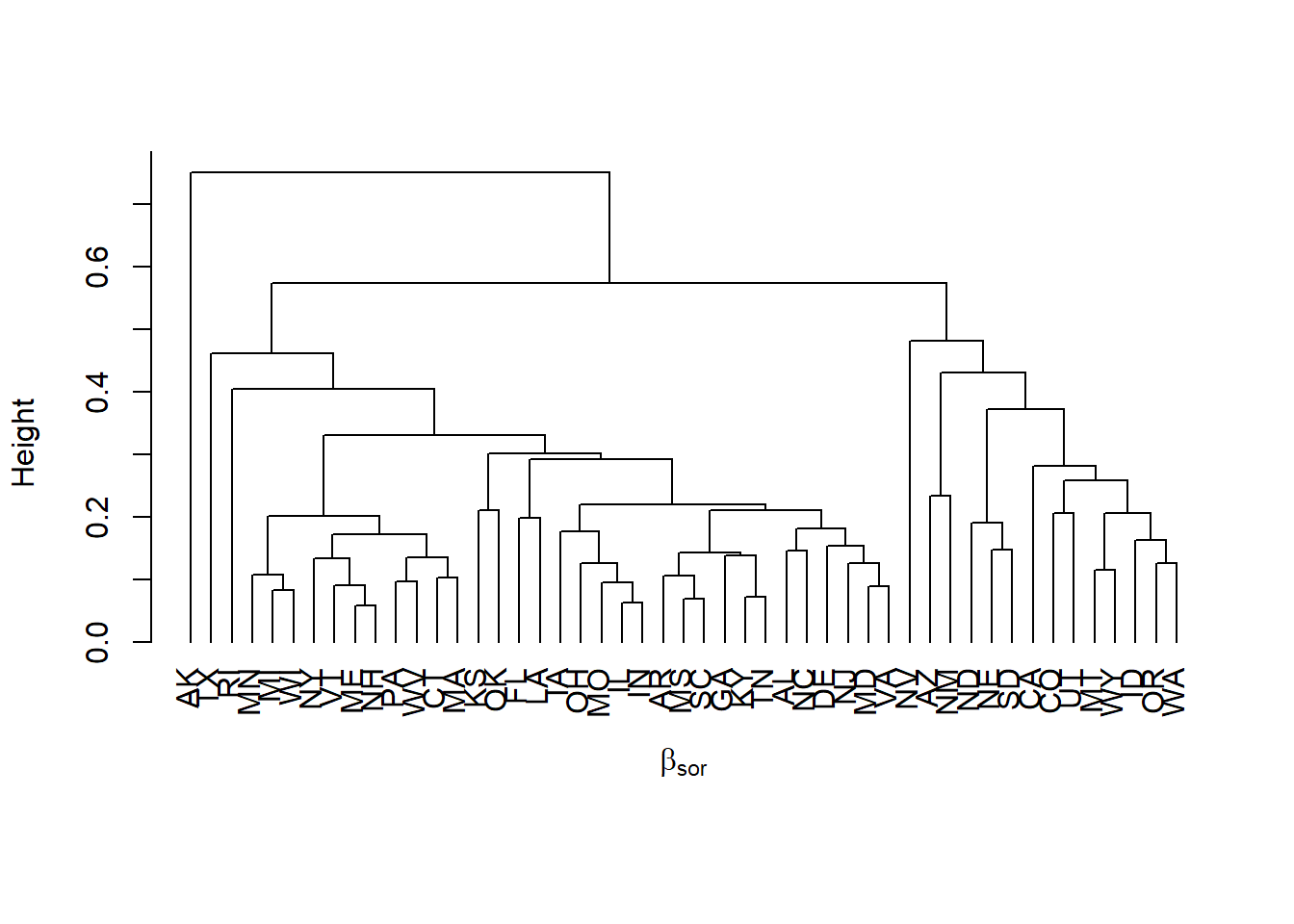
plot(hclust(bp2000$beta.sor, method="average"), hang=-1, main='', sub='', xlab='')
title(xlab=expression(beta[sor]), line=0.3)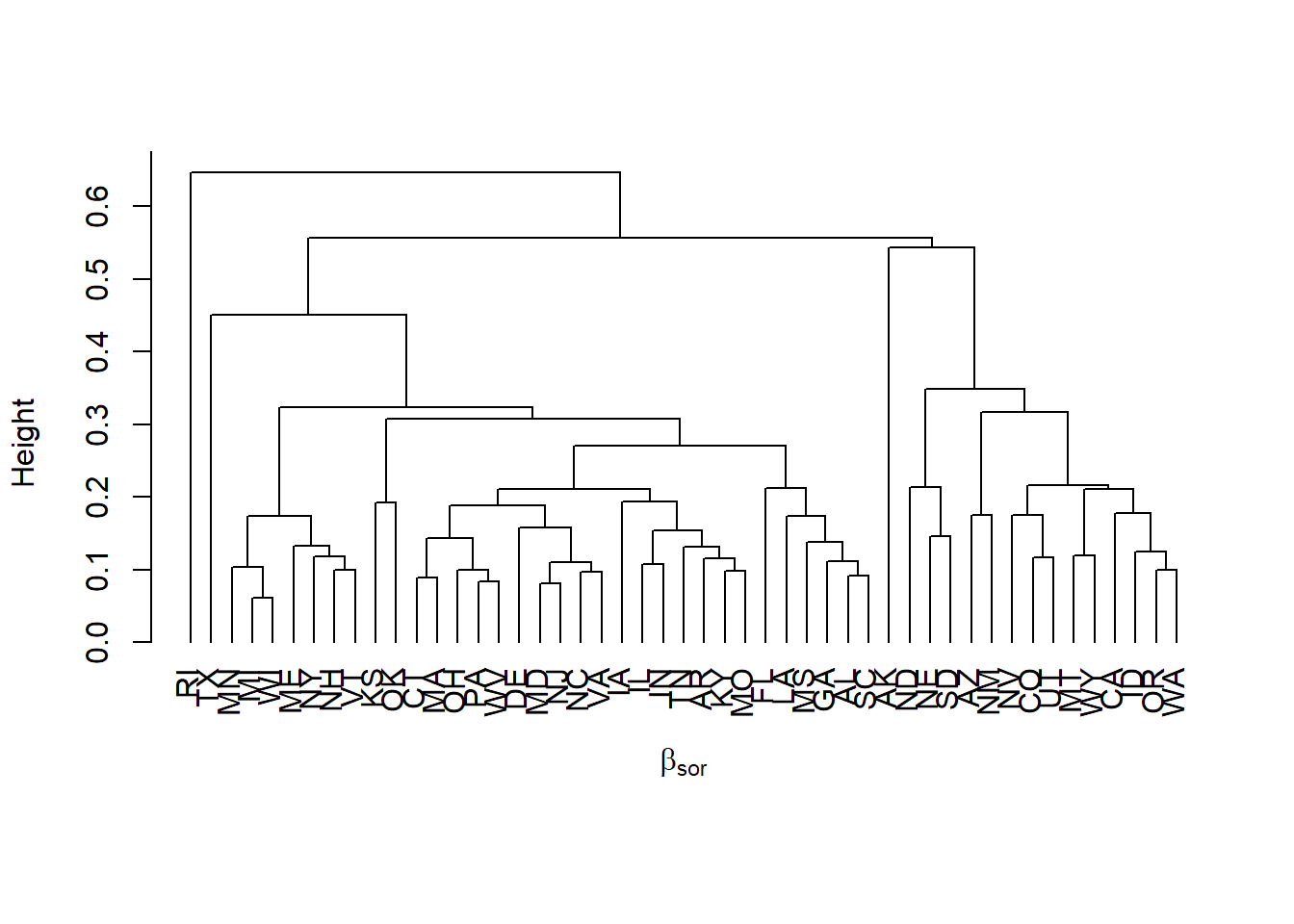
Para entender melhor o que torna as comunidades distintas é necessário entender o padrão dos valores dos componentes encontrados. Para isso podemos agrupar os valores de turnover e nestedness encontrados em cada comparação par-a-par de 2 locais diferentes em 2 períodos diferentes.
require(tidyverse)
#Acessando componentes
turnover<- as.matrix(bp1980$beta.sim) ##Para acessar o componente turnover
nestedness<- as.matrix(bp1980$beta.sne)##Para acessar o componente nestedness
#Manipulando os dados
library(reshape)
turnover<-melt(turnover)
nestedness<-melt(nestedness)
turnover<- data.frame(turnover, component = "turnover")
nestedness<- data.frame(nestedness, component = "nestedness")
df1<- bind_rows(turnover, nestedness)Para representar os valores dos componentes encontrados utilizaremos um gráfico de densidade utilizando o pacote ggplot2()
ggplot(data=df1, aes(group = component,fill=component, x = value)) +
geom_density(adjust=1.5, alpha = .8)+ theme_classic() + labs()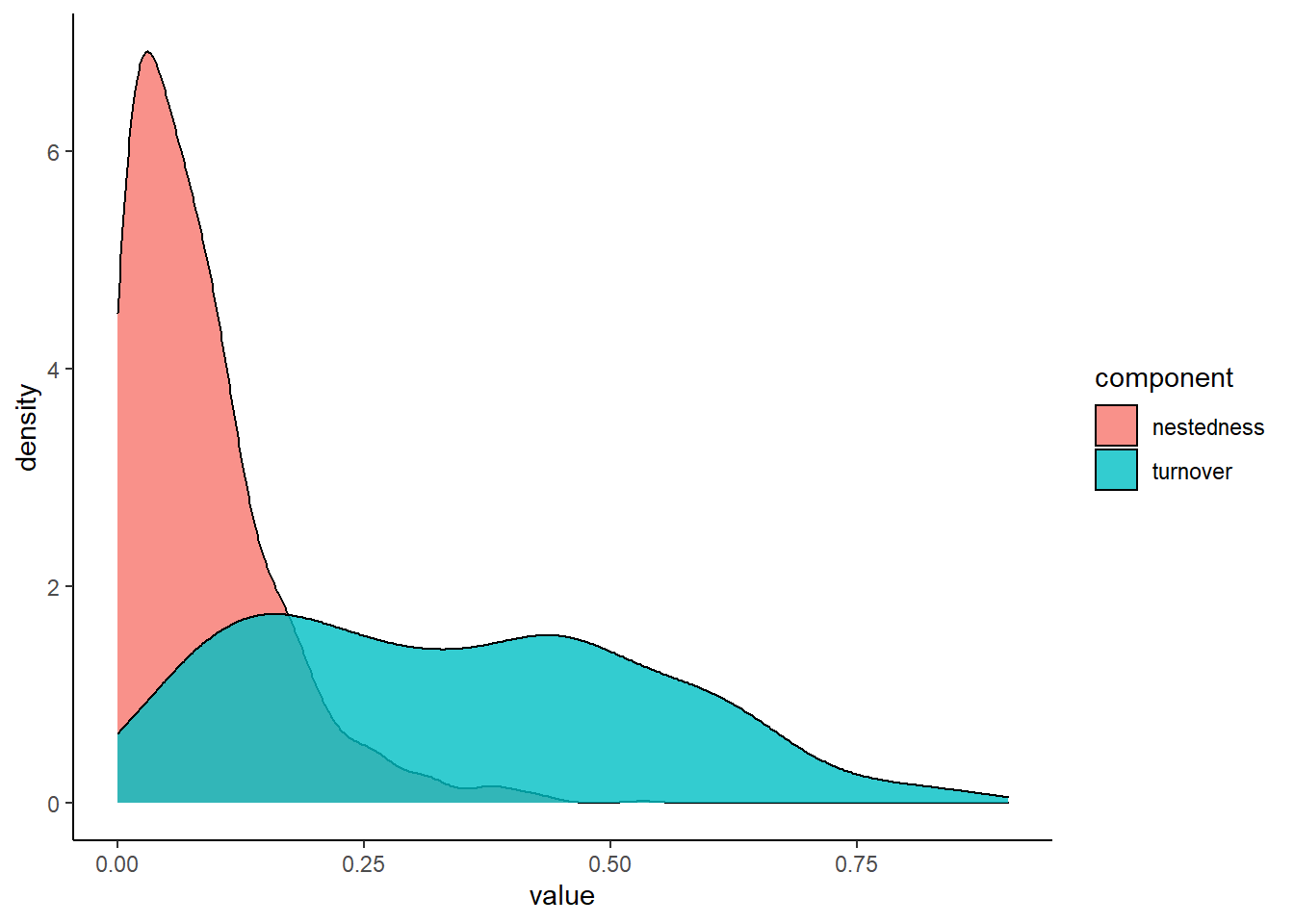
Podemos perceber que o componente nestedness possuem geralmente menores valores (0 - 0.25), dessa forma a distinção dessas comunidades é explicada principalmente pelo componente turnover, ou seja, pela reposição (substituição) de espécies entre um local e outro.
Qualquer dúvida, correção ou sugestão pode ser encaminhada para gfellipe5@gmail.com
Referências
Baselga, Andrés, and C David L Orme. 2012. “Betapart: An R Package for the Study of Beta Diversity.” Methods in Ecology and Evolution 3 (5). Wiley Online Library: 808–12.